- 2011-10-07 (金) 14:27
- DBCLS
外部コンテンツと連携して「統合検索」
今回、GGRNAを公開してから最大のアップデートをおこないました。
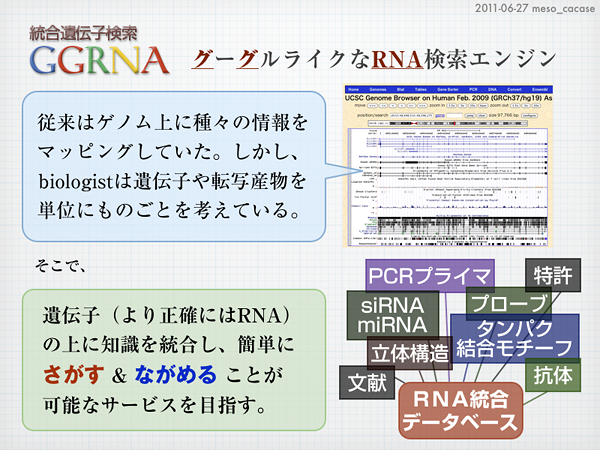
GGRNAのトップページをよく見ると「統合遺伝子検索」と銘打っているわけですが、今までのGGRNAは「RefSeqの全文検索」以上のものではありませんでした。では、「統合・・・」とはどういうことなのか。mesoが目指しているのは、様々なコンテンツを(ゲノムではなく)転写産物に紐付けて「さがす」&「ながめる」ことができる仕組みです。
今回のアップデートでは、GGRNA内部でデータを保持する方法を書きかえ、RefSeq以外のコンテンツを転写産物に紐付けて扱えるようにしています。手始めにGene Ontologyによるアノテーション情報と、酵素EC番号の情報とを、それぞれNCBI Entrez Geneから抽出してRefSeqのtranscriptに統合、GGRNAで検索できるようにしました。
Gene Ontologyで検索
アポトーシス関連遺伝子を表すGene OntologyのID、GO:0006915 で検索(→ GGRNA検索)。
ヒットした転写産物をクリックします。各転写産物に紐付けられた情報を見ることができます。
GGRNAは、実はこのテキストを全文検索して GO:0006915 という部分を見つけているだけなので、[apoptosis] で検索してもOK(→ GGRNA検索)。上記の GO:0006915 で検索した場合と同じ件数がヒットします。括弧をつけずに apoptosis で検索すると、Gene Ontology情報以外のところに apoptosis という単語が含まれるものが全部ヒットしてしまうので4000件以上になります。
それでは困るという場合、「転写産物に紐付けされた外部コンテンツ」のみを対象に検索するには anot: タグ(annot: , annotation: と書いてもよい)を使います(e.g. anot:GO:0006915 → GGRNA検索)。ただし、anot:apoptosis で検索した場合(→ GGRNA検索)は GO:0006915 [apoptosis] だけでなく、GO:0006916 [anti-apoptosis] とか GO:0042981 [regulation of apoptosis] もヒットします。
なお、スペースを含む場合はダブルクオートで囲みます(e.g. anot:“regulation of apoptosis” → GGRNA検索)。
酵素EC番号で検索
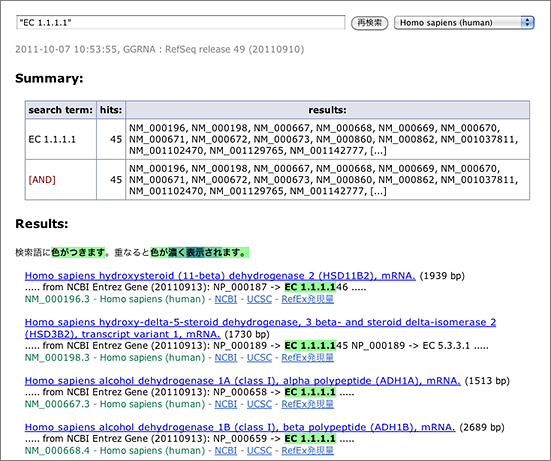
アルコールデヒドロゲナーゼ、EC 1.1.1.1 で検索(→ GGRNA検索)。anot: タグを使う場合はECの後にスペースがあるのでダブルクオートで囲み、anot:“EC 1.1.1.1” とします(→ GGRNA検索)。
EC 1.1.1.1 だけでなく、EC 1.1.1.146 や EC 1.1.1.145 がヒットしているのはご愛敬。何とかします。
なお、Gene Ontologyによるアノテーションや酵素EC番号以外にも、様々なコンテンツを今後統合していく予定です。10/5に行われたトーゴーの日シンポジウム2011ではGGRNAで疾患関連の情報やSNP、タンパクのモチーフなどを見たいという要望も頂いており、さっそく検討しています。
トップページURLを変更
トップページを http://GGRNA.dbcls.jp/ に変更し、このURLで本格運用することにしました。GGRNAの部分は小文字でも可。一般的にドメイン名は大文字小文字を区別しないルールになっています。なお、旧アドレスは新アドレスに転送されます。
RefSeq 49にアップデート、ホヤを追加
RefSeq Release 49 (Sep, 2011) にアップデートしました。同時に @wakuteka さんのリクエストでホヤCiona intestinalisを追加。ただし現時点では情報が充実していないようで、NM_* が901件に対して XM_* (predicted) が13041件でした。RefSeqのヘルプによると、RefSeq ID(アクセッション番号)の先頭が NM_ のものは「Transcript products; mature messenger RNA (mRNA) transcripts」で、XM_ のものが「Transcript products; model mRNA provided by a genome annotation process; sequence corresponds to the genomic contig」となっています。つまり XM_ のほうはRNAの分子としてまだ確認されていないもの、という言い方ができると思います。
塩基配列検索を強化
3ミスマッチまで許容して塩基配列を検索できる seq3: というタグを用意しました。相補鎖を3ミスマッチまで検索する comp3: 、両方の鎖を3ミスマッチまで検索する both3: も使えます。ただし短い配列を検索すると非常にたくさんの配列がヒットして時間がかかるので17塩基以上を推奨します。
ちなみに「caagaagagattgtg」という15塩基の配列を、完全一致検索、1ミスマッチ、2ミスマッチ、3ミスマッチまで検索、としていくとヒット件数は約10倍ずつ増えていきます。
- 「caagaagagattgtg」で検索(→ GGRNA検索)….. 2件
- 「seq1:caagaagagattgtg」で検索(→ GGRNA検索)….. 28件
- 「seq2:caagaagagattgtg」で検索(→ GGRNA検索)….. 365件
- 「seq3:caagaagagattgtg」で検索(→ GGRNA検索)….. 3522件
なお、GGRNAでは他にもいろいろな検索タグを用意しています。目的に応じて利用すれば効率的に検索できるでしょう。検索タグの一覧はヘルプのページにあります。
- GGRNAヘルプ — http://GGRNA.dbcls.jp/help.html
- Newer: トーゴーの日シンポジウム2011
- Older: アミノ酸配列クイズ
Trackbacks:0
- Trackback URL for this entry
- /archives/1371/trackback
- Listed below are links to weblogs that reference
- GGRNAの「統合検索」始動 from mesoの実験ノート